Los investigadores de UC San Diego han introducido Multi-Scale Integrated Cell (MuSIC), una tecnología que combina microscopía, bioquímica e inteligencia artificial, y revela componentes celulares previamente desconocidos que pueden proporcionar nuevas pistas sobre el desarrollo y la enfermedad humanos. (Presentación conceptual del artista.) Crédito: Universidad de California, San Diego Health Sciences
La tecnología basada en IA está revelando componentes celulares previamente desconocidos que pueden proporcionar nuevas pistas sobre la evolución y la enfermedad humanas.
La mayoría de las enfermedades humanas se remontan a partes defectuosas de la célula: un tumor puede crecer porque un gen no se ha traducido con precisión en una proteína específica o surge una enfermedad metabólica porque las mitocondrias no se activan correctamente, por ejemplo. Pero para comprender qué partes de una célula pueden fallar en una enfermedad, los científicos primero necesitan una lista completa de las partes.
Al combinar técnicas de microscopía, bioquímica e inteligencia artificial, los investigadores de la Facultad de Medicina de la Universidad de California en San Diego y sus colaboradores han dado lo que creen que puede ser un gran avance en la comprensión de las células humanas.
La tecnología, conocida como Multi-Scale Integrated Cell (MuSIC), fue descrita el 24 de noviembre de 2021 en naturaleza temperamental.
«Si imaginara una célula, probablemente se imaginara el diagrama de colores en un libro de biología celular, con mitocondrias, retículo endoplásmico y núcleo. ¿Pero es esa toda la historia? Trey Edecker, PhD, profesor de la Universidad de California, San Diego». School of Medicine y el Morris Cancer Center, dijeron. «Ciertamente no». «Los científicos han reconocido desde hace mucho tiempo que hay más cosas que no sabemos de las que sabemos, pero ahora tenemos una manera de mirar más a fondo».
Ideker dirigió el estudio con Emma Lundberg, Ph.D., del KTH Royal Institute of Technology en Estocolmo, Suecia y la Universidad de Stanford.
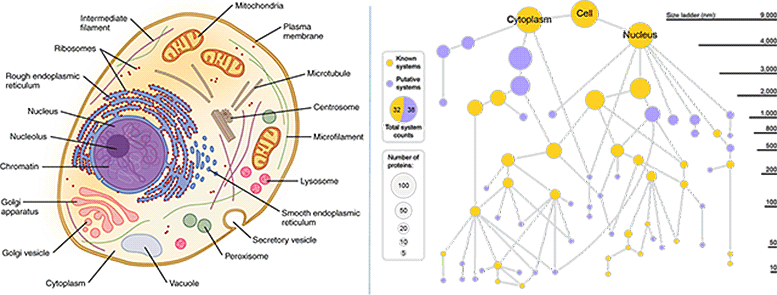
Izquierda: los diagramas de las celdas de los libros de texto convencionales indican que todas las partes son visibles y están claramente marcadas. (Crédito: OpenStax / Wikimedia). Derecha: Un nuevo mapa celular generado por la tecnología MuSIC revela varios componentes nuevos. Los nodos dorados representan componentes celulares conocidos, mientras que los nodos morados representan componentes nuevos. El tamaño del nódulo refleja el número de proteínas distintas en este componente. Crédito: Universidad de California, San Diego Health Sciences
En el estudio piloto, MuSIC reveló casi 70 componentes encontrados en la línea celular del riñón humano, la mitad de los cuales nunca se habían visto antes. En un ejemplo, los investigadores descubrieron un grupo de proteínas que forman una estructura desconocida. Trabajando con el colega de UCSD, Jin Yu, Ph.D., finalmente determinaron que la estructura es un nuevo complejo de proteínas que se unen ARN. Es probable que el complejo participe en el empalme, un evento celular importante que permite la traducción de genes en proteínas y ayuda a determinar qué genes se activan y en qué momento.
El interior de las células, y las muchas proteínas que están allí, generalmente se estudian utilizando uno de dos métodos: microscopía o correlación biofísica. Mediante imágenes, los investigadores agregan etiquetas fluorescentes de diferentes colores a las proteínas de interés y siguen sus movimientos y asociaciones a través del campo de visión del microscopio. Para observar las conexiones biofísicas, los investigadores podrían usar un anticuerpo específico de una proteína para sacarla de la célula y ver a qué más se une.
El equipo ha estado interesado en mapear el funcionamiento interno de las células durante muchos años. Lo que se diferencia de MuSIC es el uso del aprendizaje profundo para mapear una célula directamente a partir de imágenes de microscopía celular.
«La combinación de estas técnicas es única y poderosa porque es la primera vez que se combinan medidas a escalas completamente diferentes», dijo el primer autor del estudio, Yue Qin, estudiante de posgrado en bioinformática y biología de sistemas en el laboratorio de Ideker.
Los microscopios permiten a los científicos ver, al nivel de una micra, el tamaño de algunos orgánulos, como las mitocondrias. Los elementos más pequeños, como proteínas individuales y complejos de proteínas, no se pueden ver a través de un microscopio. Las técnicas bioquímicas, que comienzan con una sola proteína, permiten a los científicos alcanzar la escala nanométrica. (Un nanómetro es una mil millonésima parte de un metro, o 1000 micrones).
Pero, ¿cómo se cierra esta brecha entre la escala nanométrica y la escala micrométrica? «Siempre ha sido un gran obstáculo en las ciencias biológicas», dijo Edeker, quien también es el fundador de la Iniciativa del Mapa de Células de Cáncer de la Universidad de California y el Centro de San Diego para Biología Computacional y Bioinformática. «Resulta que se puede hacer esto con IA: mirar datos de múltiples fuentes y pedirle al sistema que los agregue en un modelo celular».
El equipo entrenó la plataforma MuSIC AI para observar todos los datos y crear un modelo celular. El sistema aún no ha asignado el contenido de las celdas a ubicaciones específicas, como el esquema de un libro de texto, en parte porque sus ubicaciones no son necesariamente fijas. En cambio, las ubicaciones de los componentes son fluidas y cambian según el tipo de celda y la situación.
Edecker señaló que se trataba de un estudio piloto de la prueba MuSIC. Solo observaron 661 proteínas y un tipo de célula.
«El siguiente paso obvio es inflar toda la célula humana y luego pasar a diferentes tipos de células, personas y especies», dijo Edecker. «En última instancia, podemos comprender mejor la base molecular de muchas enfermedades al comparar lo que es diferente entre células sanas y enfermas «.
Referencia: “Mapa multiescala de la estructura celular que incorpora imágenes de proteínas e interacciones” por Yu Chen, Edward L. Hotlin, Casper F. Winsens, Maya L. Guztaila, Ludivine Wachul, Marcus R. Kelly, Stephen M. Blue, Van Zing, Michael Chen, Leah F. Shaffer, Catherine Lecon, Anna Backstrom, Laura Pontano Weitz, John J. Lee, Wei Ouyang, Sophie N. Liu, Tian Zhang, Erica Silva, Jisoo Park, Adriana Petty, Jason F. Kreisberg, Stephen B . Gigi, Jianzo Ma, J. Wade Harper, Jane W.U., Dennis LJ Lafontaine, Emma Lundberg y Trey Edecker, 24 de noviembre de 2021, naturaleza temperamental.
DOI: 10.1038 / s41586-021-04115-9
Los coautores son: Maya L. Guztaila, Marcus R. Kelly, Stephen M. Adriana Pitea, Jason F. Kreisberg, UC San Diego; Edward L. Hotlin, Laura Pontano Weitz, Tian Zhang, Stephen B. Gigi, J. Wade Harper, Escuela de Medicina de Harvard; Casper F. Winsnes, Anna Bäckström, Wei Ouyang, Instituto Real de Tecnología de KTH; Ludivine Wacheul, Denis LJ Lafontaine, Université Libre de Bruxelles; y Jianzhou Ma, Universidad de Pekín.
La financiación para esta investigación provino, en parte, de los Institutos Nacionales de Salud (Subvenciones U54CA209891, U01MH115747, F99CA264422, P41GM103504, R01HG009979, U24HG006673, U41HG009889, R01HL137223, Fundación Consejo de Investigación Sueco R01HG00464CA Erutling). , la Universidad Libre de Bélgica en Bruselas, el Programa Conjunto Europeo de Enfermedades Raras, la Région Wallonne, la Internationale Brachet Stiftung y el Procedimiento COST de Epitran (subvención CA16120).
Divulgaciones: Trey Ideker es cofundador, miembro del Consejo Asesor Científico y tiene una participación en Data4Cure, Inc. Jin Yu es cofundador y miembro de la junta del Consejo Asesor Científico, accionista y asesor pagado de Locanabio y Eclipse BioInnovations. Yu también es profesor invitado en la Universidad Nacional de Singapur. Los términos de estos acuerdos han sido revisados y aprobados por la Universidad de California en San Diego de acuerdo con sus políticas de conflicto de intereses. Emma Lundberg es miembro de los Consejos Asesores Científicos en Biología y Cartografía, Biotecnología Nautilus e Interline Therapeutics y tiene intereses comunes. J. Wade Harper es cofundador del Consejo Asesor Científico y tiene una participación en Caraway Therapeutics. Harper es también asesor científico fundador de terapias interdisciplinarias.

«Jugador. Wannabe evangelista de la cerveza. Practicante de la cultura pop. Amante de los viajes. Defensor de las redes sociales».






More Stories
Primer vuelo del astronauta Boeing Starliner: actualizaciones en vivo
Virus gigante inusual descubierto en Austria
Científicos de Cambridge revelan una nueva teoría sobre los orígenes de los componentes básicos de la vida